Sean P. Gordon, Bruno Contreras-Moreira, Joshua J. Levy, Armin Djamei, Angelika Czedik-Eysenberg, Virginia S. Tartaglio, Adam Session, Joel Martin, Amy Cartwright, Andrew Katz, Vasanth R. Singan, Eugene Goltsman, Kerrie Barry, Vinh Ha Dinh-Thi, Boulos Chalhoub, Antonio Diaz-Perez, Ruben Sancho, Joanna Lusinska, Elzbieta Wolny, Candida Nibau, John H. Doonan, Luis A. J. Mur, Chris Plott, Jerry Jenkins, Samuel P. Hazen, Scott J. Lee, Shengqiang Shu, David Goodstein, Daniel Rokhsar, Jeremy Schmutz, Robert Hasterok, Pilar Catalan, John P. Vogel
Nature Communications
DOI: https://doi.org/10.1038/s41467-020-17302-5
Streszczenie artykułu:
Niniejszy artykuł jest pokłosiem realizowanego przez Międzynarodową Inicjatywę Brachypodium projektu naukowego, finansowanego ze środków Community Science Program US Department of Energy, a także szeregu innych, podjętych w różnych krajach inicjatyw badawczych w tym finansowanych przez Narodowe Centrum Nauki i wykonywanych przez Zespół Cytogenetyki i Biologii Molekularnej Roślin IBBiOŚ projektów Maestro oraz Harmonia.
Brachypodium hybridum jest jednorocznym, allotetraploidalnym przedstawicielem modelowego rodzaju traw Brachypodium (kłosownica), a jego domniemanymi gatunkami rodzicielskimi są B. distachyon oraz B. stacei. Z racji swej natury, B. hybridum zyskał ostatnio duże znaczenie w badaniach gatunków mieszańcowych w kontekście lepszego zrozumienia struktury i ewolucji ich genomów – zarówno jądrowych, jak i organellarnych. Analizy tego typu są często trudne, ponieważ w przypadku naturalnych form mieszańcowych nie jest wiadomo które konkretnie genotypy gatunków rodzicielskich wzięły udział w tworzeniu allopoliploida. W celu rozróżnienia pomiędzy przedpoliploidyzacyjnym efektem założyciela, a procesami ewolucyjnymi mającymi miejsce już po powstaniu gatunku mieszańcowego, w niniejszej pracy oparto się na analizie pan-genomu B. hybridum oraz jego domniemanych gatunków rodzicielskich. Wyniki wykonanych w ramach tej pracy kompleksowych badań porównawczych sugerują, że większość zmienności składu genowego w pan-genomie B. hybridum spowodowana jest zmiennością obserwowaną także w pan-genomach gatunków rodzicielskich. Analizy polimorfizmów na poziomie zmian jednego nukleotydu (tzw. SNP), genomów chloroplastowych oraz podsekwencji (tzw. k-merów) powiązanych z ruchomymi elementami genetycznymi sugerują że do powstania B. hybridum doszło w wyniku dwóch niezależnych zdarzeń, odpowiednio ok. 1,4 mln i ok. 140 tyś lat temu. Jednym z najważniejszych wniosków płynących z tej pracy jest to, że procesy popoliploidyzacyjne zachodzące u tego mieszańca międzygatunkowego polegają na stopniowej akumulacji zmian genomicznych i – poza sytuacją obserwowaną w odniesieniu do genów kodujących 18S-5,8S-25S rRNA – na braku specyficznej genomowo dominacji lub supresji aktywności transkrypcyjnej genów. Co istotne, niezastosowanie w opisywanych badaniach analiz pan-genomicznych spowodowałoby istotne przeszacowanie liczby zmian genomicznych mających miejsce już po skrzyżowaniu się B. distachyon z B. stacei i powstaniu B. hybridum.
Częścią badań przedstawionych w niniejszej pracy były wykonane przez pracowników Zespołu Cytogenetyki i Biologii Molekularnej Roślin (Joanna Łusińska, Elżbieta Wolny, Robert Hasterok) szczegółowe porównawcze analizy struktury i ewolucji tak całych kariotypów, jak i poszczególnych chromosomów i ich fragmentów wykonane na poziomie cytomolekularnym w oparciu o technikę wielobarwnej fluorescencyjnej hybrydyzacji in situ z wykorzystaniem specyficznych chromosomowo sond molekularnych.
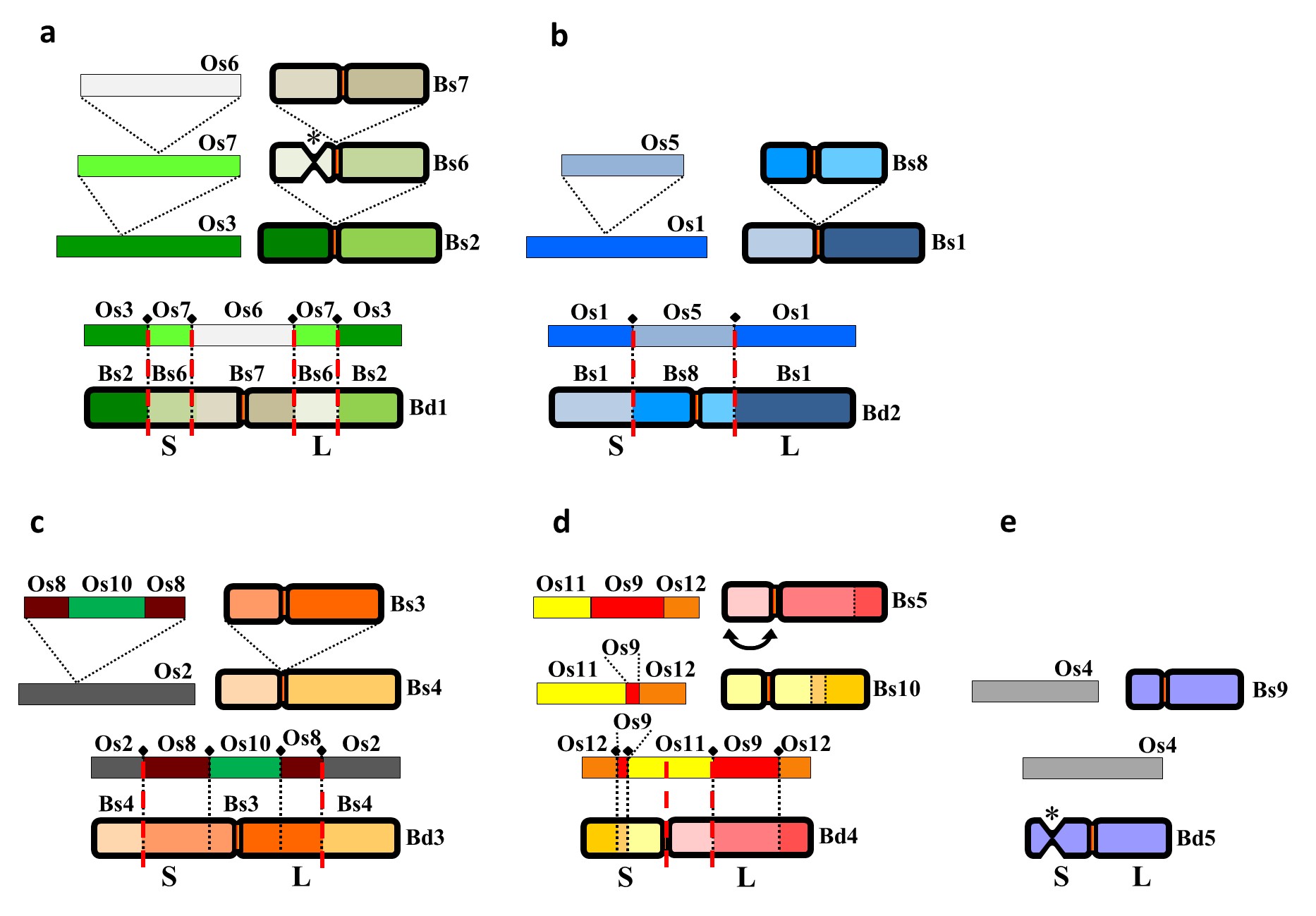
Opis ryciny
Wnioskowanie na temat ewolucji chromosomów w oparciu o analizy cytomolekularne z wykorzystaniem porównawczego prążkowania chromosomów metodą BAC-FISH z wykorzystaniem sond specyficznych chromosomowo. Poszczególne kolory obrazują syntenię pomiędzy pięcioma chromosomami Brachypodium distachyon (genotyp referencyjny Bd21) i odpowiednimi chromosomami B. stacei (genotyp ABR114) oraz tzw. odpowiednikami ancestralnych chromosomów ryżu (Oryza sativa). a-c Zależność między chromosomami B. distachyon Bd1 do Bd3 i odpowiednimi chromosomami B. stacei może być wyjaśniona jako efekt zajścia serii fuzji całych odpowiedników ancestralnych chromosomów ryżu w obszary centromerowe (Bd1: Bs7→Bs6→Bs2; Bd2: Bs8→Bs1; Bd3: Bs3→Bs4). d Chromosom Bd4 jest synteniczny względem chromosomów Bs5 oraz Bs10. Dodatkowo w chromosomie Bd4 zaszła inwersja pericentryczna (obejmująca obszar centromeru). d Chromosom Bd5 jest wysoce kolinerany względem chromosomu Bs9. Gwiazdki wskazują lokalizację zawierającego locus 35S rDNA przewężenia wtórnego/satelity w chromosomach Bd5 i Bs6.